- En Ejecución
- UTEM/VRIP | LCLI24-06
Development of a Predictive Web Tool for Coding Potential in Bacterial RNA Transcripts and Its Application in Biomining Organisms
- Raul Arias Carrasco
- 06/2025 – 06/2027
- Biología Computacional
Información del proyecto
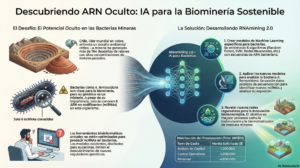
El proyecto busca desarrollar y optimizar modelos de machine learning específicos para bacterias que permitan predecir el potencial codificante de transcritos de ARN. Estos modelos serán integrados en una versión actualizada de la herramienta web RNAmining 2.0.
Como aplicación biológica, el proyecto se enfoca en la identificación y análisis funcional de nuevos ARN no codificantes (ncRNAs) en la bacteria usada en biominería Acidithiobacillus ferrooxidans, utilizando datos transcriptómicos públicamente disponibles y análisis computacionales avanzados.
¿Por qué es importante?
Los ncRNAs cumplen roles regulatorios clave en bacterias, pero están pobremente anotados, especialmente en microorganismos extremófilos de interés biotecnológico. Las herramientas actuales están optimizadas principalmente para eucariotas, lo que limita su uso en bacterias.
Este proyecto aborda esa brecha mediante el desarrollo de modelos predictivos específicos para bacterias, mejorando la precisión en la identificación de ncRNAs y permitiendo descubrir nuevos mecanismos regulatorios asociados a la adaptación a ambientes extremos.
Impacto y resultados
- Científico: Expansión del conocimiento sobre regulación génica mediada por ncRNAs en bacterias biomineras.
- Tecnológico: Desarrollo de RNAmining 2.0, una herramienta web de acceso gratuito con modelos bacterianos optimizados.
Aplicado: Potencial impacto en biominería, bioremediación y sostenibilidad ambiental mediante una mejor comprensión de la regulación genética en microorganismos usados en minería. - Formación de capital humano: Participación activa de estudiantes de postgrado en investigación computacional avanzada.